

Hi-C技术使全基因组水平的染色质互作分析成为可能,推动了对compartment、TAD和染色质环等三维基因组结构及其调控功能的认识【1–5】。然而,生成高质量Hi-C数据在实验成本和技术门槛上的要求限制了其在单细胞和空间组学中的广泛应用。现有的计算预测方法虽已取得进展,但在跨细胞类型泛化、单细胞数据稀疏性适应以及多组学数据依赖等方面仍存在不足,受限于多组学配套需求、跨细胞类型泛化不足以及对数据稀疏性的适应能力有限等问题。
2026年4月14日北京大学临床医学高等研究院(细胞稳态与衰老性重大疾病北京研究中心)/北京大学肿瘤医院吴华君、北京大学第三医院徐明和北京大学肿瘤医院王玉娟共同通讯在 Nature Communications 上发表了题为 "Hi-Compass: a depth-aware deep learning framework for predicting cell-type-specific 3D genome organization from single-cell to spatial resolution" 的研究论文。该工作提出了深度学习框架Hi-Compass,以ATAC-seq数据为唯一的细胞类型特异性输入,实现了从bulk到单细胞、再到空间分辨率的跨尺度Hi-C接触图谱预测。

图1:论文截图
Hi-Compass基于CNN-Transformer架构,以ATAC-seq信号作为唯一的细胞类型特异性输入,同时结合DNA序列和泛细胞类型CTCF结合谱进行Hi-C接触图谱预测。模型在训练阶段引入不同测序深度的ATAC-seq数据并通过深度嵌入编码深度信息,从而适应bulk、单细胞和空间组学之间差异极大的数据覆盖度。在多细胞类型联合训练策略下,Hi-Compass对未见过的细胞类型具备zero-shot预测能力。
系统性benchmark显示,Hi-Compass在Hi-C图谱相关性、染色质环恢复等一系列一致性等指标上优于Akita、C.Origami、Epiphany和ChromaFold等已有方法,尤其在跨细胞类型泛化场景中表现突出。结合多细胞类型联合训练,Hi-Compass对训练集之外的细胞类型同样具备稳定的预测能力。
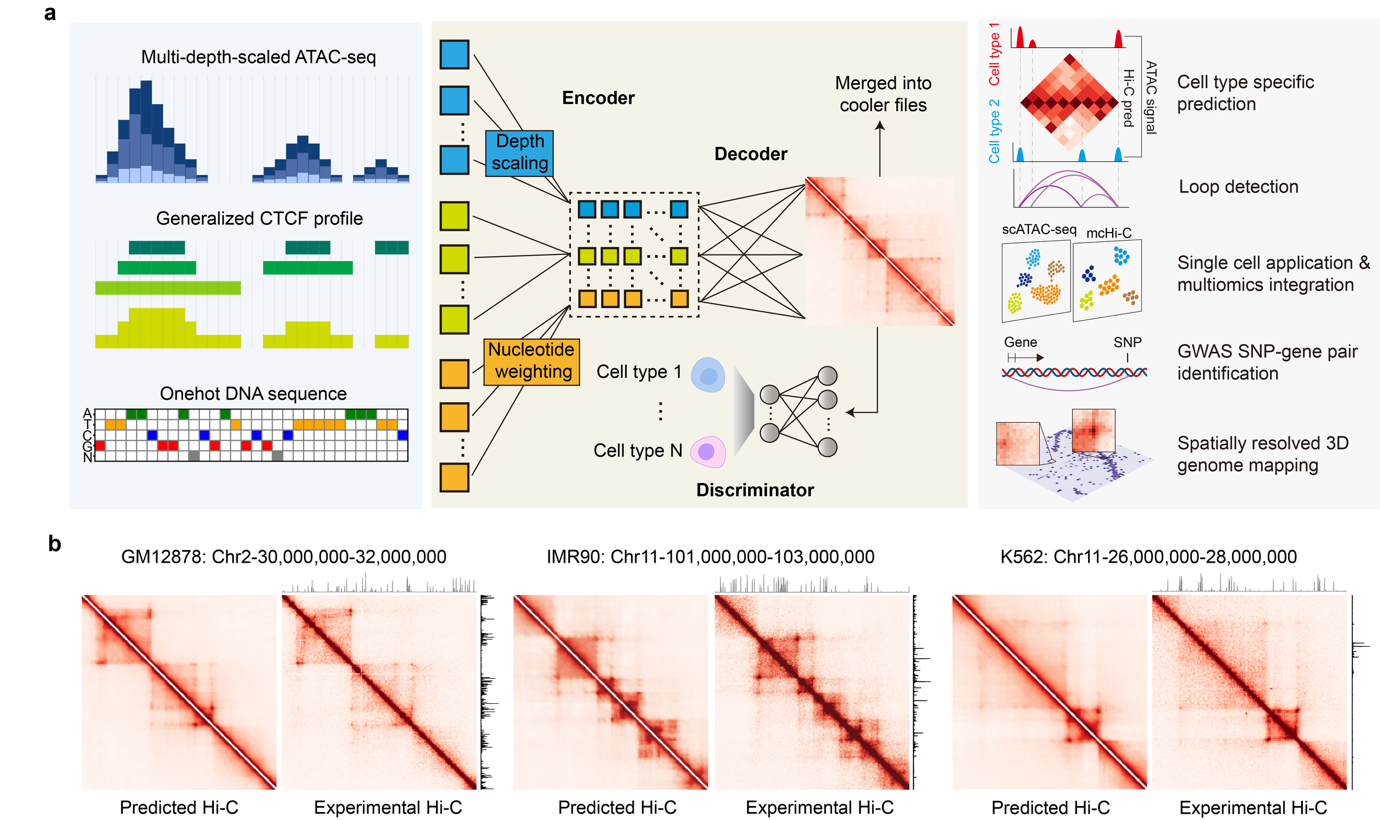
图2:Hi-Compass模型架构与预测示例
作者团队将Hi-Compass应用于PBMC免疫细胞亚群scATAC-seq数据和胚胎心脏发育multiome数据,成功解析了细胞类型特异性的染色质互作图谱,并将GWAS非编码变异与候选靶基因进行了系统性关联。在人类海马组织的spatial ATAC-seq数据上,Hi-Compass实现了空间分辨的染色质互作预测。此外,通过对小鼠基因组的fine-tuning,作者验证了Hi-Compass的跨物种泛化能力。
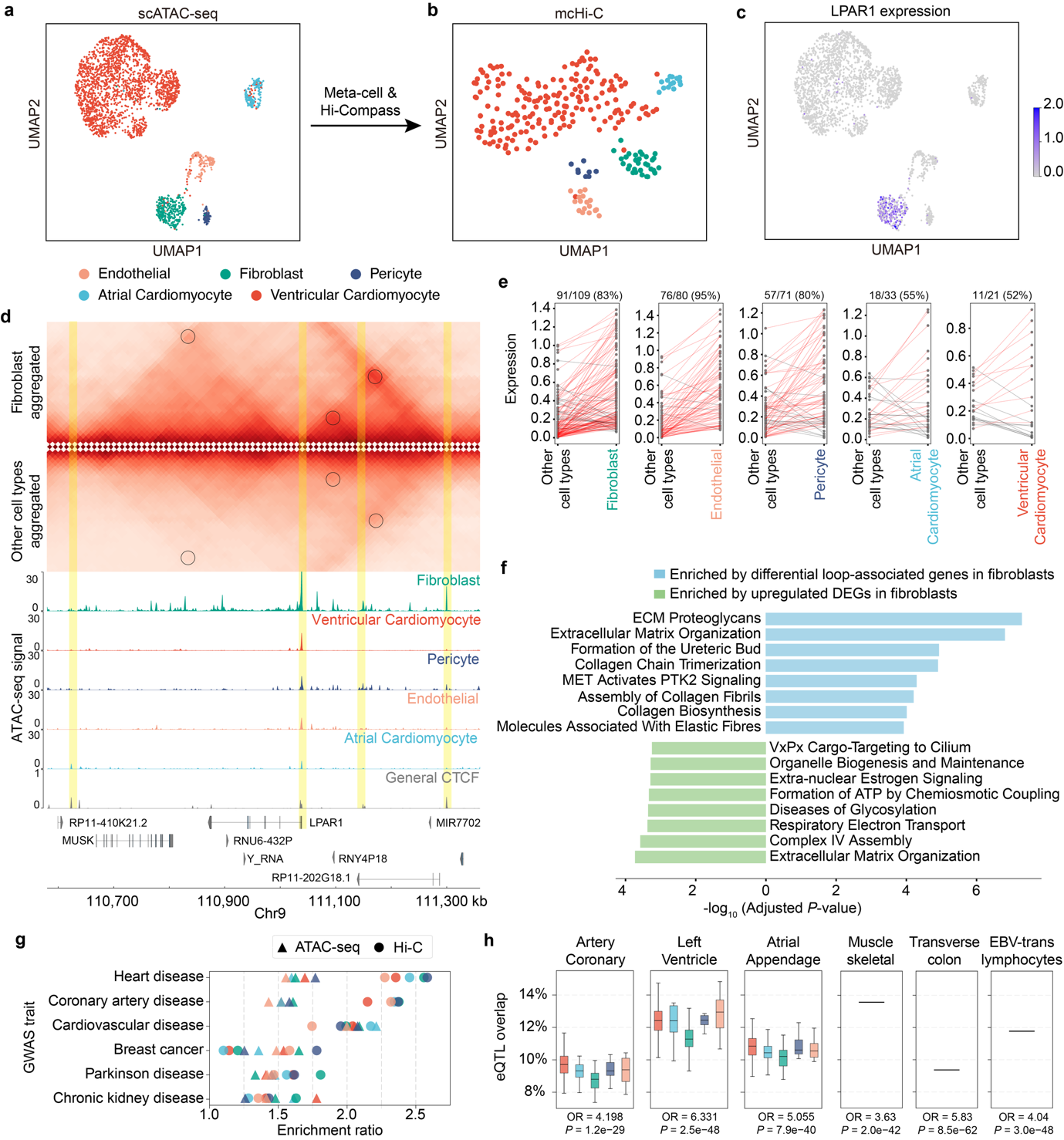
图3:基于Hi-Compass解析多深度细胞类型特异性染色质三维结构
该工作为三维基因组研究提供了一个统一的、覆盖bulk—单细胞—空间多尺度的预测框架,拓展了在缺少Hi-C实验数据的条件下系统性研究染色质三维结构的能力。
本论文的共同通讯作者为北京大学临床医学高等研究院(细胞稳态与衰老性重大疾病北京研究中心)/北京大学肿瘤医院吴华君研究员、北京大学第三医院徐明教授和北京大学肿瘤医院王玉娟博士;北京大学肿瘤医院孙源辰、北京大学第三医院蒋文杰和北京大学肿瘤医院蔡康文为本文的共同第一作者。
共同通讯作者
吴华君

研究员, 博士生导师 现任北京大学临床医学高等研究院/北京大学肿瘤医院助理教授。
主要研究领域为计算基因组学与三维基因组学,聚焦于利用计算方法解析染色质空间结构及其在基因调控和疾病中的功能。
References
1. Bonev B, Cavalli G. Organization and function of the 3D genome. Nature Reviews Genetics 2016, 17:661–678.
2. Dekker J, Mirny L. The 3D genome as moderator of chromosomal communication. Cell 2016, 164:1110–1121.
3. Hafner A, Boettiger A. The spatial organization of transcriptional control. Nature Reviews Genetics 2023, 24:53–68.
4. Lieberman-Aiden E, et al. Comprehensive mapping of long-range interactions reveals folding principles of the human genome. Science 2009, 326:289–293.
5. Rao SSP, et al. A 3D map of the human genome at kilobase resolution reveals principles of chromatin looping. Cell 2014, 159:1665–1680.